抗体是机体免疫系统识别和防御病原体感染的重要分子,在感染性疾病防治、肿瘤免疫治疗以及生物药物开发等领域具有广泛应用价值。近年来,随着单克隆抗体药物的快速发展,如何快速、准确地获取抗体序列信息,已成为抗体研究与开发中的关键技术问题。然而,传统抗体测序方法通常依赖杂交瘤细胞或B细胞的基因信息,不仅实验周期较长,而且在部分研究场景中难以获得对应的细胞来源,从而限制了抗体药物的研发效率。
针对这一挑战,我院夏宁邵教授、袁权教授团队建立了一种基于质谱的高通量抗体从头测序技术(XA-Novo)。该技术整合了创新的样品处理方法(SP-MEGD)与人工智能驱动的序列组装算法(Fusion),实现了抗体序列的高精度重建。在多种已知序列抗体数据集上的测试结果表明,Fusion算法能够实现抗体重链与轻链序列的准确覆盖,并在抗原结合关键区域(CDR)中保持精确序列重建。相比之下,传统算法在复杂区域往往会出现序列缺失或拼接错误,从而影响抗体功能解析。进一步研究还表明,XA-Novo不仅适用于单个抗体测序,还能够同时解析多个抗体混合样品。在包含两种或三种抗体的混合体系中,该方法仍能准确区分并重建每个抗体的完整序列,整体准确率超过99.5%。为验证XA-Novo在真实研究场景中的应用能力,研究团队进一步对多种序列未知的多个抗体蛋白样品进行序列解析,经基因工程重组表达获得的重组抗体,在体内外实验中表现出与原始抗体相当的生物学效能。
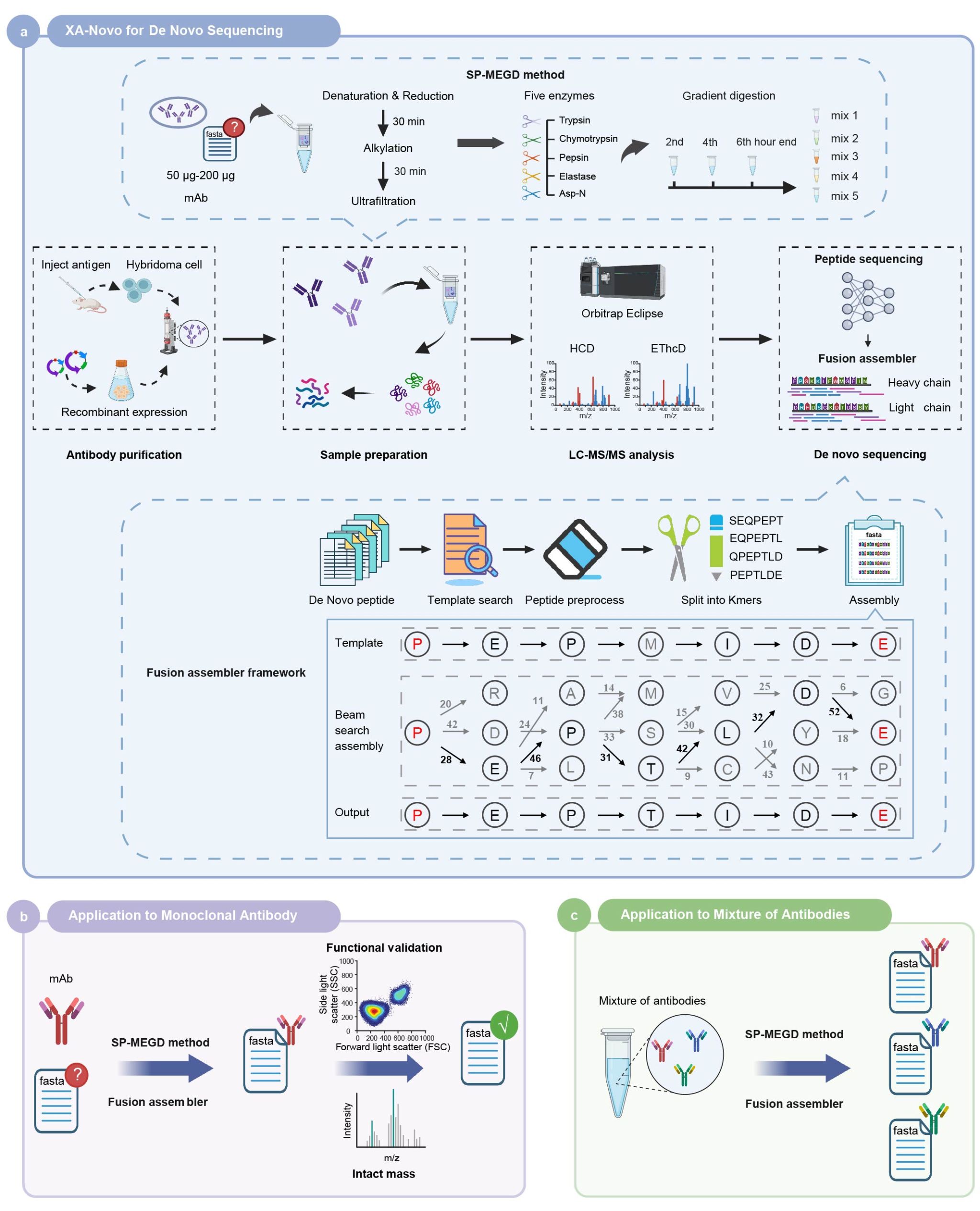
图1. XA-Novo工作流程
此外,为了方便科研人员使用该技术,团队还开发并上线了XA-Novo网页平台(https://xa-novo.com/)。研究人员只需上传质谱数据(.mgf格式)并填写相应的物种信息,平台即可调用预训练模型与Fusion组装算法,对数据进行抗体序列解析,并生成包含候选序列及CDR区域注释的分析结果报告,为后续抗体序列确认与功能研究提供重要参考。
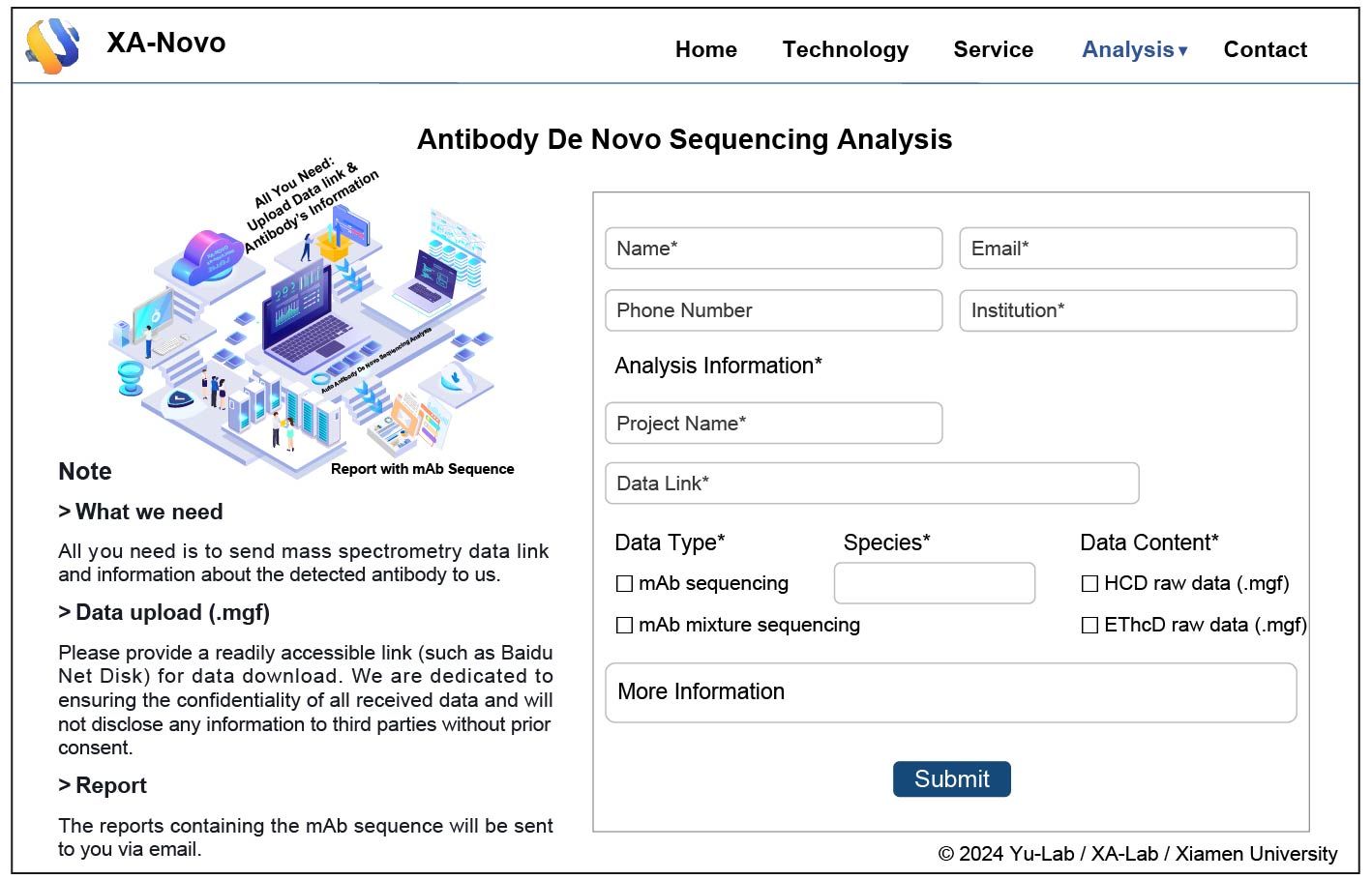
图2. XA-Novo网页平台
综上,XA-Novo通过整合创新的多酶梯度消化策略(SP-MEGD)、深度学习肽段测序算法以及新型序列组装算法(Fusion),实现了单克隆抗体及混合抗体的高精度序列重建。该技术为抗体序列解析提供了一种高效可靠的新方法,未来有望在抗体发现、免疫组学研究、生物药物质量控制以及抗体工程等领域发挥重要作用,也可为抗体相关研究和药物开发提供关键技术支撑。
近日,该研究成果以题为“XA-Novo: high-throughput mass spectrometry-based de novo sequencing technology for monoclonal antibodies and antibody mixtures”的研究论文在线发表于《自然•通讯》(Nature Communications)。我院熊悦婷、肖瑾,健康医疗大数据国家研究院江文彬为该论文的共同第一作者。我院夏宁邵教授、袁权教授、熊悦婷,健康医疗大数据国家研究院俞容山为该论文的共同通讯作者。该研究获得国家科技重大专项、国家自然科学基金、福建省自然科学基金、厦门市自然科学基金、传染病疫苗研发全国重点实验室/翔安创新实验室科技项目的资助与支持。
论文链接:https://www.nature.com/articles/s41467-026-70496-y
(公共卫生学院)